
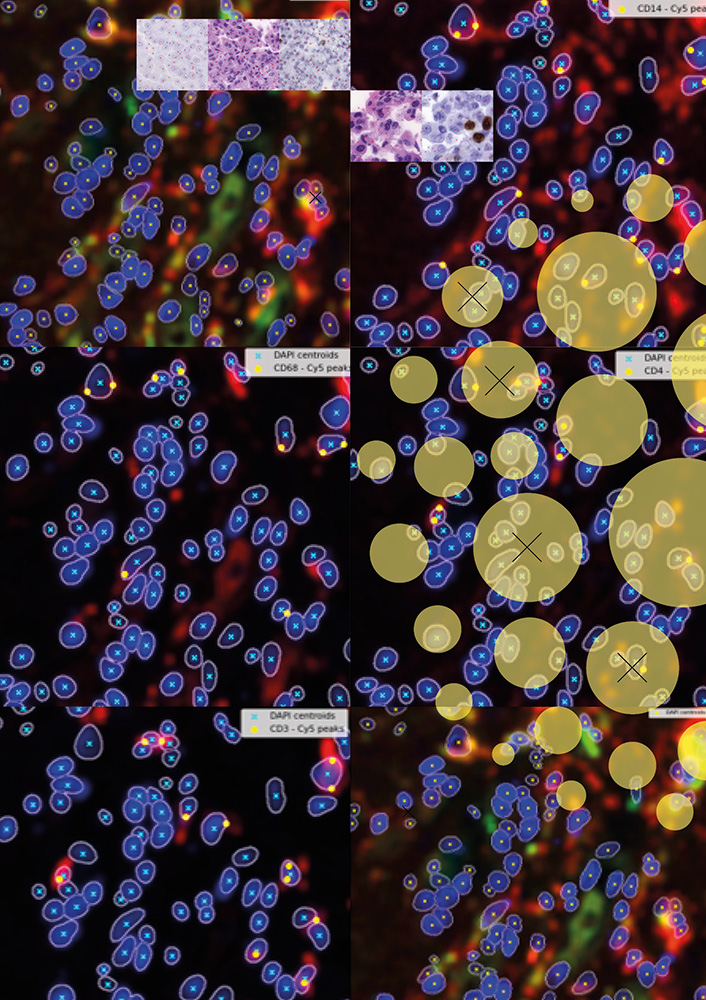
Code de segmentation des noyaux utilisés dans la recherche sur l’analyse d’images de pathologie numérique, 2024 [MIT License].
# nuclei segmentation in histopathology slide
thresholded = image > otsu(image)
labels = measure.label(thresholded)
nuclei = morphology.remove_small_objects (labels, min_size=100)
À propos du code
En pathologie, les spécialistes examinent traditionnellement des échantillons de tissus au microscope pour identifier les maladies. Aujourd’hui, des programmes informatiques aident cette analyse, effectuant des tâches qui reposaient autrefois uniquement sur l’expertise humaine. Cet extrait de code illustre cette transformation ; quatre lignes qui segmentent les noyaux cellulaires, étape fondamentale du diagnostic.
Ces lignes fonctionnent comme un assistant numérique au microscope. Le code identifie d’abord les cellules et l’espace vide, comme distinguer des taches d’encre sur du papier blanc. Ensuite, il regroupe les pixels connectés pour former des noyaux complets, de la même façon que nous identifions des types de nuage. Enfin, il élimine le bruit, ne conservant que les structures significatives. Le résultat est une carte que les ordinateurs peuvent analyser, transformant l’image complexe vue par le pathologiste en données organisées permettant aux systèmes d’intelligence artificielle de détecter des motifs cancéreux, classifier les maladies ou prédire les réponses aux traitements.
Cet extrait marque un tournant médical, un témoignage de soins de santé devenus computationnels, avec du code source intégré dans des processus guidant des décisions vitales. Il reflète notre dépendance croissante aux machines, par nécessité : des millions de patients, trop peu de pathologistes formés. Écrit pour des prototypes de recherche, ce code accompagne désormais le diagnostic du cancer, la découverte de médicaments et le dépistage par intelligence artificielle. Cette transformation de la biologie vers les données, de l’observation humaine vers l’analyse computationnelle, impacte notre compréhension de la pratique médicale – où des fragments de code, une fois mis à l’échelle, portent à la fois un pouvoir et une responsabilité éthique.
Cette transformation de la biologie vers les données, de l’observation humaine vers l’analyse computationnelle, impacte notre compréhension de la pratique médicale – où des fragments de code, une fois mis à l’échelle, portent à la fois un pouvoir et une responsabilité éthique.
BIOGRAPHIE
Esha Sadia Nasir, doctorante à l’Université de Warwick, est spécialiste en pathologie computationnelle.
Ses recherches portent sur l’analyse d’images d’immunofluorescence multiplexée pour l’identification de biomarqueurs et l’étude de la progression des maladies. Elle développe des algorithmes pour analyser des lames d’histopathologie, contribuant ainsi aux avancées dela recherche sur le diagnostic et le traitement du cancer. Her research focuses on multiplex immunofluorescence image analysis for biomarker discovery and disease progression. She develops algorithms to analyze histopathology slides, contributing to advances in cancer diagnosis and treatment research.
#Pathologie computationnelle
#Healthcare
#Imagerie médicale
